


研究揭示馬里亞納海溝底棲生物群落結(jié)構(gòu)和多樣性區(qū)別于沖繩海槽
文章來源:深海生物學(xué)研究室 | 發(fā)布時(shí)間:2022-07-01 | 【打印】 【關(guān)閉】
近日,深海生物研究室海洋生物生態(tài)與進(jìn)化研究組在國際期刊Deep Sea Research Part I: Oceanographic Research Papers上在線發(fā)表了題為“Comparison of structure and diversity of benthic communities in the Okinawa Trough and Mariana Trench by environmental DNA metabarcoding” 的學(xué)術(shù)論文。研究利用環(huán)境DNA和高通量測序技術(shù)(即eDNA宏條形碼),分析并比較了西北太平洋兩個(gè)深海區(qū)域的底棲生物群落結(jié)構(gòu)特征和多樣性。
深海海底地域廣大,具有豐富的生物多樣性,但是長期以來由于受到采樣技術(shù)和分析手段等多種因素的限制,人們對深海生態(tài)系統(tǒng)的認(rèn)識仍然比較有限。目前有關(guān)深海生物多樣性的研究雖然很多,但是多局限于6000 m以淺的區(qū)域,深度超過6000 m的深淵區(qū)域仍然是目前地球上探索最少的生態(tài)系統(tǒng)。隨著人類活動和氣候變化對深海的影響日益嚴(yán)重,為了保護(hù)深海生態(tài)系統(tǒng),需要加快深海生物多樣性的研究步伐。
過去很多對深淵底棲生物的調(diào)查結(jié)果顯示,深淵底棲生物的豐度、多樣性和群落組成和鄰近深海或半深海環(huán)境有所不同,但這些研究主要是基于占有優(yōu)勢的大型底棲生物類群。環(huán)境DNA(eDNA)宏條形碼是評估生物多樣性的一種新方法。該方法將環(huán)境樣品(例如,沉積物、水體或空氣)和高通量測序技術(shù)結(jié)合,可以確定環(huán)境中出現(xiàn)的物種,并評估總體的生物多樣性。相比傳統(tǒng)方法,這種方法尤其適合研究微小的生物類群(例如,小型底棲動物),而這些微小生物類群在生態(tài)系統(tǒng)中往往數(shù)量龐大而且非常多樣化。近年來海洋沉積物eDNA宏條形碼研究也顯示這種方法可以幫助人們認(rèn)識深海底棲生物類群的多樣性和種群分布模式。
研究團(tuán)隊(duì)以沖繩海槽(~500-1000 m)和馬里亞納海溝(~6500 m)為研究區(qū)域,利用沉積物DNA和兩個(gè)核基因(28S和18S rRNA 基因),比較了深海陸坡和深淵海溝區(qū)域底棲生物群落結(jié)構(gòu)和多樣性。

圖1 馬里亞納海溝和沖繩海槽沉積物采樣地點(diǎn)示意圖
研究結(jié)果顯示,沖繩海槽比馬里亞納海溝具有更多的真核生物類群,而且兩個(gè)深海區(qū)域的底棲生物類群的組成是截然不同的。對28S rRNA 基因序列,在OTU水平上,僅有7% 的OTUs(Operational taxonomic units)是兩個(gè)區(qū)域共有的,而即使在科的水平上,兩個(gè)區(qū)域之間共有的科也僅占到20%左右。18S rRNA 基因也具有相似的趨勢。NMDS和聚類分析也顯示兩者間的群落組成是顯著不同的(p < 0.05)。
對兩個(gè)區(qū)域后生動物類群的分析結(jié)果也顯示沖繩海槽具有更多的后生動物門類,而且兩個(gè)區(qū)域中的優(yōu)勢動物類群明顯不同。28S rRNA基因數(shù)據(jù)顯示,刺胞動物是沖繩海槽豐度最高的動物類群(序列豐度30.5%),其次是環(huán)節(jié)動物 ;而海溝中豐度最高(46%)的動物類群是線蟲,其次是軟體動物(16.4%)。海槽區(qū)多樣性最高的為環(huán)節(jié)動物(33個(gè)OTUs,21個(gè)科);而在海溝區(qū)最多樣的是線蟲,具有21個(gè)OTUs(歸屬于10個(gè)科)。18S rRNA基因在海槽區(qū)顯示了相似的結(jié)果,但是卻發(fā)現(xiàn)在海溝中Xenacoelomorpha海洋蠕蟲類豐度最高(34.2%),其次是線蟲(22.9%),而且海溝中線蟲是多樣性最高的(19個(gè)OTUs,9個(gè)科)。
研究結(jié)果揭示了馬里亞納海溝底棲生物多樣性低于陸坡區(qū)的沖繩海槽,而且兩者具有顯著不同的底棲生物群落。環(huán)節(jié)動物是海槽區(qū)多樣性最高而且豐度較高的一大動物類群,而線蟲則是海溝區(qū)最有優(yōu)勢的動物類群。在未來的工作中,研究團(tuán)隊(duì)將繼續(xù)采集來自近岸沿海、深海平原及海溝底部的沉積物樣品,利用環(huán)境DNA方法在更大尺度上解析底棲生物從淺海到深淵的分布模式。
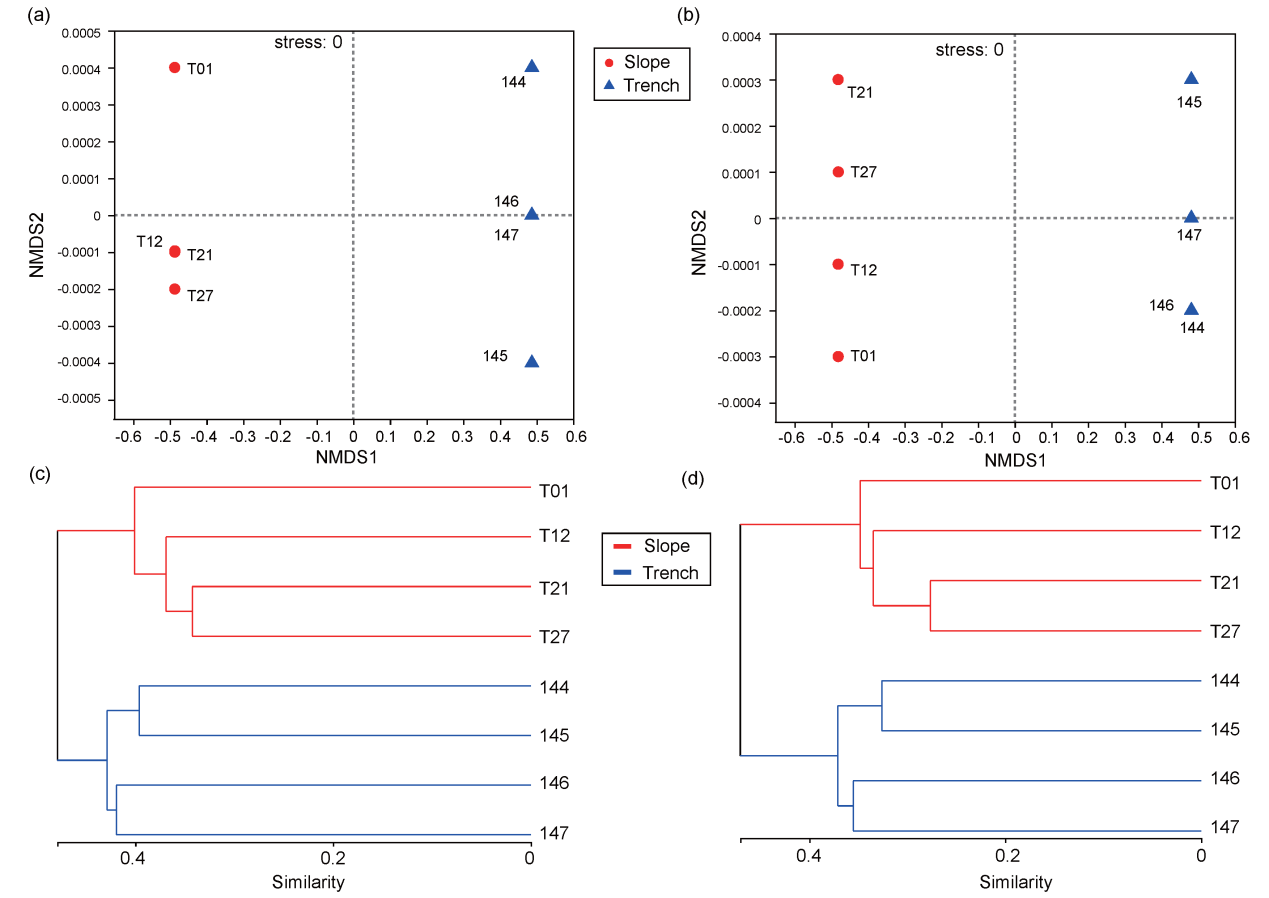
圖2 NMDS(a和b)和聚類(c和d)分析結(jié)果。其中(a)和(c)為28S rRNA基因數(shù)據(jù);(b)和(d)為18S rRNA基因數(shù)據(jù)。

圖3 沖繩海槽和馬里亞納海溝的后生動物門類的相對豐度。其中(a)和(b)為28S rRNA基因數(shù)據(jù);(c)和(d)為18S rRNA基因數(shù)據(jù)。
論文信息:
Jun Liu, Lvpei Du, Zhilei Sun, Haibin Zhang*, (2022) Comparison of structure and diversity of benthic communities in the Okinawa Trough and Mariana Trench by environmental DNA metabarcoding, Deep Sea Research Part I: Oceanographic Research Papers, 185, 103806, https://doi.org/10.1016/j.dsr.2022.103806

Copyright © 中國科學(xué)院深海科學(xué)與工程研究所 備案證號:瓊ICP備13001552號-1
 瓊公網(wǎng)安備 46020102000014號
瓊公網(wǎng)安備 46020102000014號
地址: 三亞市鹿回頭路28號 郵編:572000 網(wǎng)站維護(hù):深海所辦公室 郵箱:office@idsse.ac.cn